2019年4月17日,《Nature Protocols》(IF=12.423)在线发表题为“R-ChIPfor Genome-wide Mapping of R-loops by Using Catalytically Inactive RNASEH1”的方法学论文,金沙8888js官方陈亮研究员为该文的共同通讯作者。该工作获得了武汉大学引进人才启动经费的资助。
当由转录产生的RNA与模板DNA通过碱基互补配对形成杂合链时,另外一条非模板DNA链将处于单链状态,由此形成的三链核酸结构称为R-loop。R-loop广泛存在于细菌、真菌、植物与动物的基因组中,在基因转录、DNA复制、表观遗传修饰以及DNA损伤修复等过程中都具有重要作用,并与许多重大疾病的发生和发展密切相关,是近年来分子生物学的一个新研究热点。R-loop研究非常依赖能够准确定位与定量R-loop结构的检测技术。此前广泛应用的DRIP-seq技术主要利用识别RNA/DNA杂合链的单克隆抗体S9.6对R-loop进行体外富集,并进行建库测序。该方法可以在全基因组水平对R-loop信号进行检测,但也存在若干技术问题,包括检测信号的分辨率有限和S9.6抗体的特异性不足。此外,体外富集的DRIP-seq信号能否真实反映细胞内R-loop的水平仍存在争议。解决这些问题并进一步推动R-loop研究的进展亟待独立新技术的开发。
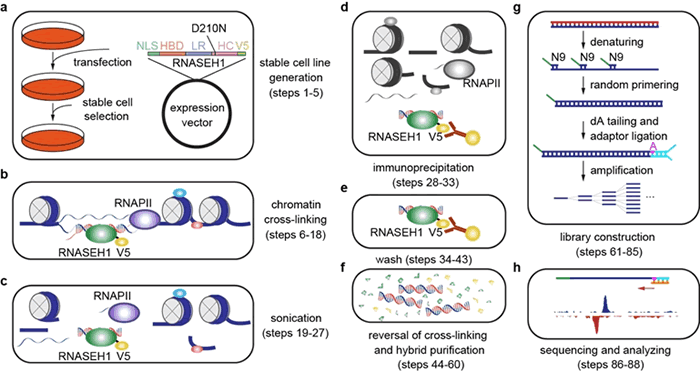
本文报道的新技术R-ChIP通过在细胞中表达RNASEH1突变体(RNASEH1为特异性切割R-loop的内切酶,经突变改造后失去催化功能,但其R-loop结合活性被保留),可特异性识别体内形成的R-loop,通过富集和文库的建立与测序,即可绘制细胞内R-loop的全基因组图谱。该方法具有三个特点:1)内源性,直接在细胞体内捕获R-loop;2)高分辨率,检测精度在200个碱基左右;3)高特异性,研究者可以使用RNASEH1催化/结合位点双突变体的R-ChIP数据做为阴性对照,进一步提高R-loop识别信号的特异性。陈亮研究员在此前的工作中利用R-ChIP技术对R-loop的动态变化进行监测,发现RNA聚合酶的停滞是促进R-loop形成的重要原因,并发现转录区域DNA的GC分布以及非模板链形成的二级结构对R-loop的形成具有重要影响(Chen et al, 2017, Mol Cell)。在R-loop与重大疾病关系的研究中,陈亮研究员运用R-ChIP技术发现在骨髓增生异常综合症(MDS)中,多种剪接因子的突变均造成造血干细胞R-loop水平的紊乱,从而影响基因组的稳定性与细胞功能维持(Chen et al, 2018, Mol Cell),提示R-loop异常可能是MDS疾病发生的重要机制,为MDS与白血病的研究和治疗提供了全新视角。